本文摘要: 很多朋友对于宏基因组测序分析流程和宏基因组测序分析流程PPT不太懂,今天就由小编来为大家分享,希望可以帮助到大家,下面一起来看看吧!
很多朋友对于宏基因组测序分析流程和宏基因组测序分析流程PPT不太懂,今天就由小编来为大家分享,希望可以帮助到大家,下面一起来看看吧!
宏基因组关联分析的思路和方法
〖One〗、在宏基因组关联分析的应用中,关注宿主、环境和微生物组成的复合状态,逐步研究菌群的功能、相关因子、内在动力和干扰,实现靶向微生物组的调控。宏基因组关联分析在实际生产中的应用旨在实现靶向微生物研究的目标,通过关注共有的菌群,实现对健康状态的精准调控。
〖Two〗、宏基因组关联分析(MWAS)是一种研究环境微生物组与特定表型之间关系的方法。通过分析环境(如肠道、水体、土壤)中的所有微生物DNA序列,并进行一系列数据处理,我们可以获得微生物的物种组成和数量信息,进而结合网络、通路等进行深入分析。
〖Three〗、在疾病研究中,进行差异比较分析,识别疾病与健康人群微生物群落组成与功能差异,寻找疾病相关微生物标志物。构建微生物互作网络,揭示微生物间的潜在关系,为理解微生物群落功能提供新视角。
〖Four〗、宏基因组分析是一种研究技术,它能够揭示特定环境中的所有生物体的遗传信息。这种技术不仅包括微生物,还包括真菌、病毒和原生动物等,通过分析它们的DNA或RNA,科学家可以了解环境中的生物多样性及其相互作用。全基因组关联分析(GWAS)则是一种广泛应用于遗传学领域的研究方法。
〖Five〗、聚类分析和主成分分析等方法的运用,揭示了群落结构的差异,帮助我们理解不同个体间的微生物组成差异。通过与宿主的健康状况、饮食习惯等进行关联分析,我们能够挖掘潜在的因果关系,为揭示微生物与宿主健康之间的联系提供科学依据。
宏基因组测序原理?
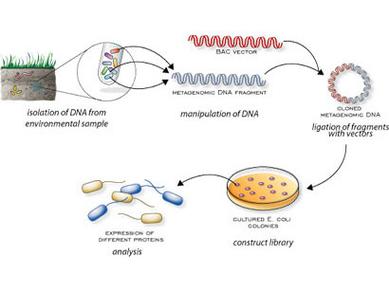
〖One〗、以及微生物与环境间的联系。宏基因组测序不依赖于微生物的分离培养,扩展了微生物资源利用范围,提供环境微生物群落研究的有效工具。宏基因组测序原理是将微生物基因组DNA打断成小片段,通过PCR扩增后进行组装,可鉴定到种甚至菌株水平。
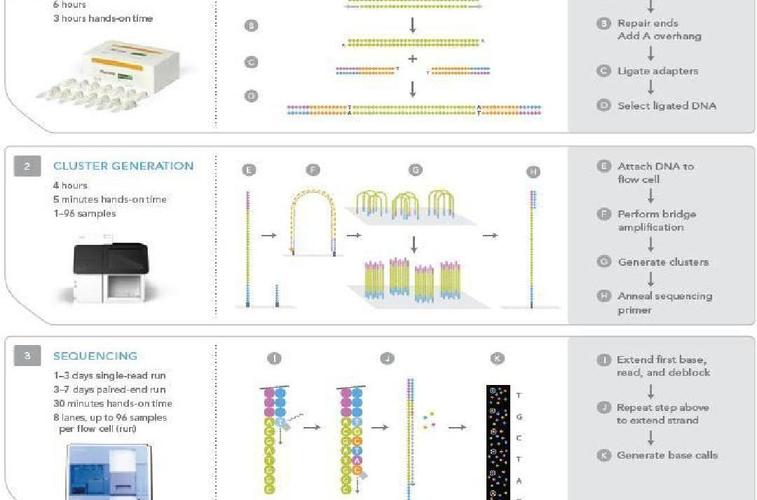
〖Two〗、以典型的二代测序平台Illumina为例,其测序原理是基于桥式聚合酶链式反应(PCR)的边合成边测序,特点是读长短、准确性高。和一代测序相比,具有测序速度快、准确性高以及成本低的优良特性。
〖Three〗、宏基因组分析是一种研究技术,它能够揭示特定环境中的所有生物体的遗传信息。这种技术不仅包括微生物,还包括真菌、病毒和原生动物等,通过分析它们的DNA或RNA,科学家可以了解环境中的生物多样性及其相互作用。全基因组关联分析(GWAS)则是一种广泛应用于遗传学领域的研究方法。
〖Four〗、农业领域中,宏基因组测序揭示了微生物与植物互作、农业耕作、施肥处理与土壤微生物群落的关系。环境领域,宏基因组测序可用于研究雾霾处理、污水治理、石油降解、酸性矿水处理及海洋环境,甚至在极端环境下微生物类群的探索。
〖Five〗、进行宏基因组测序的第一步是DNA提取。从环境样本中提取DNA是至关重要的步骤,因为这直接决定了后续分析的质量。提取完成后,会针对特定的DNA区域,如16S或18S,进行扩增。这些区域的选取基于其在所有微生物中高度保守的特性,能够有效反映微生物种群的组成。扩增后的DNA产物会被建库并进行测序。
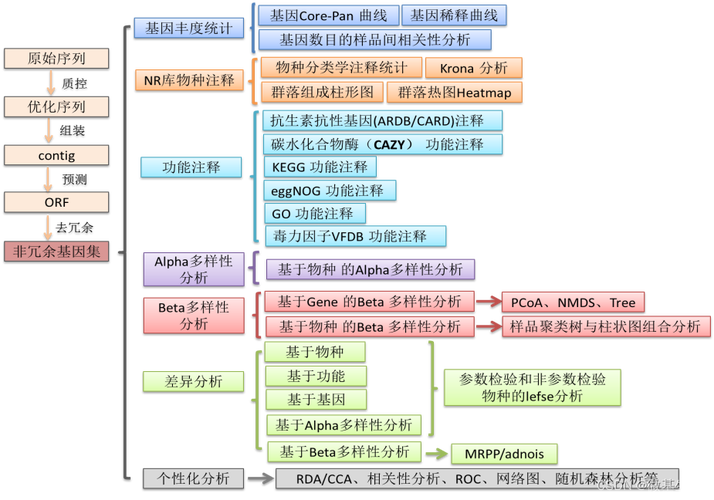
在宏基因组测序中,如何进行数据的生物信息学分析?
〖One〗、数据的生物信息学分析在宏基因组测序中至关重要。首先,研究人员需对原始测序数据进行质控,去除低质量序列,确保分析结果的准确性和可靠性。随后,使用拼接软件将短序列拼接成长序列(或contigs),此步骤对未培养微生物分析尤为重要。
〖Two〗、测序环节使用高通量测序平台,如Illumina、PacBio等,产生大量测序数据。最后,进行数据的生物信息学分析,包括数据质量控制、序列比对、物种注释、功能预测等,以获得有意义的生物学信息。
〖Three〗、另外,进行了粪便、土壤、沉积物和人类口腔样本的稀释曲线测试,结果显示1G Clean data可以达到物种注释的饱和度。
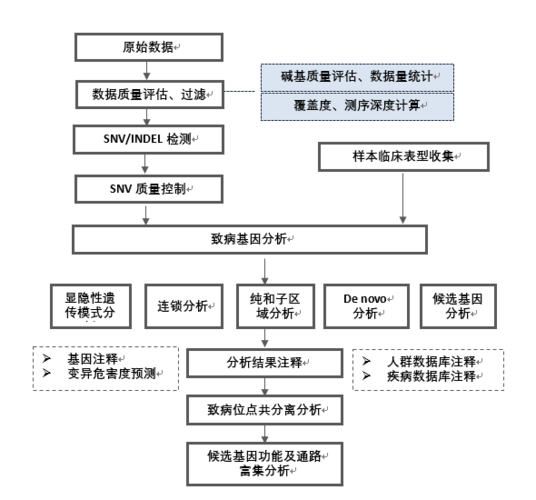
求助哪位大神知道全外显子测序的流程和原理
在WES过程中,首先需要从样本中提取DNA,并对其进行测序。随后,通过生物信息学工具对测序数据进行分析,以识别出感兴趣的外显子区域。进一步的分析步骤包括变异检测、注释以及功能研究,最终确定哪些基因变异可能与特定疾病相关。
外显子捕获测序和转录组测序都是针对基因组上转录区域进行测序,但是外显子捕获测序针对已有基因组信息的物种,而转录组分析既能针对已有基因组信息的物种,也能针对没有基因组信息的新物种,因此,两者的分析存在一定的差异:『1』分析的目标区域有所不同。
全外显子组测序是将人类基因按照特定检测方法进行测序,再通过分析来实现的。NGS作为核心技术,实为一种捕获测序,捕获理解为一种选取过程,依据所需检测的基因数量来实施。基于NGS平台的捕获测序原理,形成了三大常见方案:Panel、全外显子(WES)与全基因组(WGS)测序,如下图。
全外显子组测序(WES)针对基因全部外显子部分进行测序。技术原理包括切割基因组DNA为小片段,使用靶向杂交探针获取外显子序列,随后进行测序。
基因组学的测序方法(DNA)
全基因组测序(WGS)全基因组测序是指对物种细胞的完整基因组进行测序,从DNA的第一个碱基开始到最后一个碱基结束,完整检测并排列基因组序列,能鉴定出基因组中的各种类型突变。这种方法适用于没有借鉴基因组或借鉴质量不佳的生物体。近来主要有两种技术。
第3代测序技术采用直接测序方法。基因组DNA被随机切割成大约100 kb左右的片段,并与六寡聚核苷酸探针杂交。然后,驱动结合了探针的基因组文库片段通过可寻址的纳米孔阵列。通过每个孔的离子电流可独立测量,追踪电流变化确定探针杂交在每个基因组片段上的精确位置。
第一代测序技术采用荧光标记的Sanger法,这种方法不再赘述。第二代测序技术包括循环阵列合成测序法,其核心在于通过DNA聚合酶或DNA连接酶将碱基连接到DNA链上过程中释放的光学信号来间接确定序列。这要求使用昂贵的光学监测系统,并需记录、存储和分析大量光学图像,增加了仪器的复杂性和成本。
第一代DNA测序技术:以双脱氧链终止法和化学裂解法为代表。这些技术主要通过测定DNA链上不同位置的终止片段来确定整个DNA序列。双脱氧链终止法是通过使用特定的核苷酸终止子来生成一系列长度不同的DNA片段,从而得到序列信息。
第二代测序技术,例如循环阵列合成测序法,通过荧光或化学发光物质的帮助,利用光学信号间接确定DNA聚合酶或DNA连接酶将碱基连接到DNA链上过程中释放的信号。这种方法需要昂贵的光学监测系统,同时记录、存储并分析大量的光学图像,这都增加了仪器的复杂性和成本。
病毒宏基因组学(Meta-virome)
病毒宏基因组学,即Meta-virome,是宏基因组学理论与现代病毒检测技术融合的新兴领域。它关注的是样本中所有病毒及其携带遗传信息的总体,包括环境中广泛存在的病毒组成。这一研究方法尤其在病毒检测、溯源、微生物预警等领域展现其关键作用,如探索人或动物肠道、血液样本、海洋和土壤中的潜在威胁。
宏病毒组学(Viral Metagenomics)是结合宏基因组学理论与现有病毒分子生物学检测技术的新兴学科,旨在直接分析样本中所有病毒的遗传物质,快速准确鉴定病毒组成,称为“病毒组(Virome)”。
HiC测序技术:通过HiC测序技术辅助预测病毒宿主,揭示了地下水系统中病毒与宿主之间的复杂联系。宏基因组与宏病毒组测序:宏基因组测序:利用Illumina平台对地下水样本进行宏基因组测序,获取了丰富的微生物信息。
美格基因|宏病毒组知识分享
〖One〗、总之,宏病毒组学作为新兴研究领域,展现出巨大潜力与价值。美格基因的创新技术与案例研究进一步推动了宏病毒组学的发展,为病毒学研究提供有力工具与新视角。
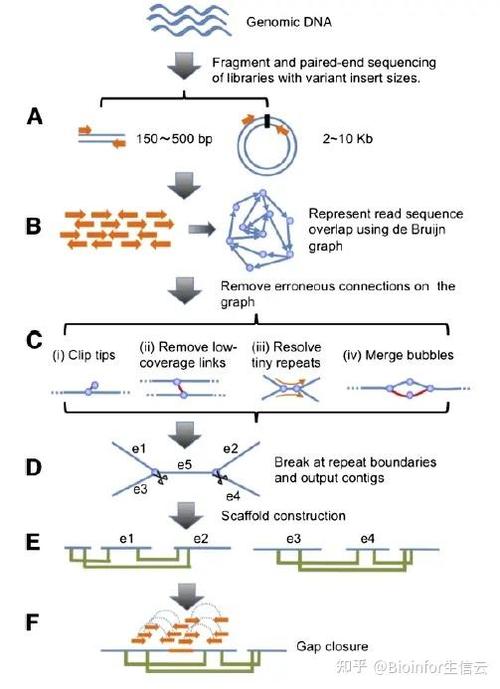
宏基因组测序分析(八)宏基因组数据组装
〖One〗、二代测序数据的组装通常按照如下步骤:短reads先经过质量控制,后进行数据清洗。随后,构建reads间的Overlap,进而使用DBG算法实现快速组装。通过此流程,组装生成的序列片段连结为基因组。
〖Two〗、宏基因组组装工具主要用于将测序结果组装成完整的基因组序列,近来市面上已有不少成熟的工具。对于宏基因组数据库和测序序列分类工具的介绍,以及对ITS和16S测序的兴趣,未来将进行深入探讨。宏基因组测序的快速发展,为微生物领域研究提供了前所未有的机遇与挑战。
〖Three〗、宏基因组测序方法主要包含三大类:基于测序结果的组装分析,基于reads直接与已知数据库比对,以及基于分箱(bin)的方法。每种方法各有优缺点,适用于不同研究需求。
关于本次宏基因组测序分析流程和宏基因组测序分析流程PPT的问题分享到这里就结束了,如果解决了您的问题,我们非常高兴。